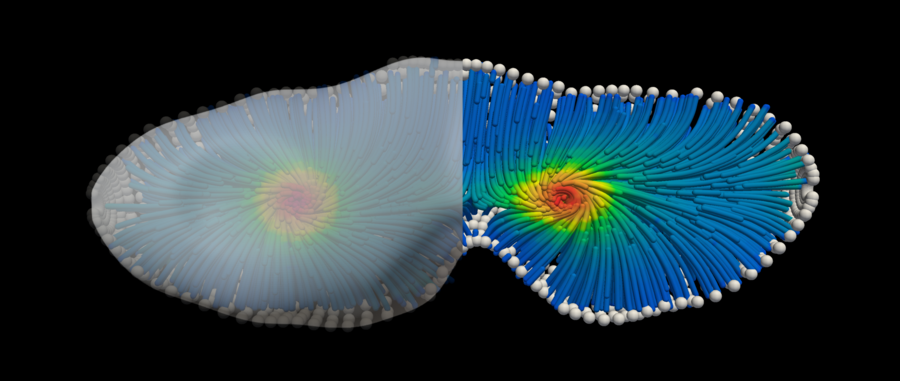
3D Simulation eines aktiven Materials in einer geometrischen Form, die einer sich teilenden Zelle ähnelt. © Singh et al. Physics of Fluids (2023) / MPI-CBG
Biologische Materialien sind aus einzelnen Komponenten zusammengesetzt, darunter winzige Motoren, die Kraftstoff in Bewegung umwandeln. Auf diese Weise entstehen Bewegungsmuster, und das Material strukturiert sich durch ständigen Energieverbrauch selbst. Solche permanent bewegten Materialien werden als "aktive Materie" bezeichnet. Die Mechanik von Zellen und Geweben lässt sich mit der Theorie der aktiven Materie beschreiben, einem wissenschaftlichen Konzept um die Form und Bewegung lebender Materialien zu verstehen. Die Theorie der aktiven Materie besteht aus vielen anspruchsvollen mathematischen Gleichungen. Wissenschaftlerinnen und Wissenschaftler des Max-Planck-Instituts für molekulare Zellbiologie und Genetik (MPI-CBG) in Dresden, des Zentrums für Systembiologie Dresden (CSBD) und der TU Dresden haben nun einen Algorithmus entwickelt und in einem Open-Source Supercomputer-Code implementiert, der die Gleichungen der Theorie aktiver Materie zum ersten Mal in realistischen Szenarien lösen kann. Diese Ergebnisse bringen uns der Lösung des jahrhundertealten Rätsels, wie Zellen und Gewebe ihre Form erhalten und dem Design künstlicher biologischer Maschinen einen großen Schritt näher.
Biologische Prozesse und Muster sind oft sehr komplex. Physikalische Theorien bieten einen präzisen und quantitativen Rahmen, um diese zu verstehen. Die Theorie der aktiven Materie bietet einen Rahmen, um das Verhalten aktiver Materie zu verstehen und zu beschreiben - Materialien, die aus einzelnen Komponenten bestehen, die einen chemischen Brennstoff ("Nahrung") in mechanische Kräfte umwandeln können. An der Entwicklung dieser Theorie waren mehrere Forschende aus Dresden maßgeblich beteiligt, unter anderem Frank Jülicher, Direktor am Max-Planck-Institut für Physik komplexer Systeme und Stephan Grill, Direktor am MPI-CBG. Mit diesen physikalischen Grundlagen lässt sich die Dynamik aktiver lebender Materie durch mathematische Gleichungen beschreiben und vorhersagen. Diese Gleichungen sind jedoch äußerst komplex und schwer zu lösen. Daher benötigen Wissenschaftlerinnen und Wissenschaftler die Leistung von Supercomputern, um lebende Materialien zu verstehen und zu analysieren. Es gibt verschiedene Möglichkeiten, das Verhalten aktiver Materie vorherzusagen. Einige konzentrieren sich auf die winzigen einzelnen Teilchen, andere untersuchen aktive Materie auf molekularer Ebene, und wieder andere untersuchen aktive Flüssigkeiten im Großen. Diese Studien helfen Wissenschaftlerinnen und Wissenschaftlern zu verstehen, wie sich aktive Materie auf verschiedenen Längenskalen im Raum und über die Zeit hinweg verhält.
Lösung komplexer mathematischer Gleichungen
Forschende aus der Arbeitsgruppe von Ivo Sbalzarini, TU-Dresden-Professor am Zentrum für Systembiologie Dresden (CSBD), Forschungsgruppenleiter am Max-Planck-Institut für molekulare Zellbiologie und Genetik (MPI-CBG) und Dekan der Fakultät Informatik der TU Dresden, haben jetzt einen Computeralgorithmus entwickelt, der die mathematischen Gleichungen aktiver Materie löst. Ihre Arbeit wurde in der Fachzeitschrift "Physics of Fluids" veröffentlicht und auf der Titelseite hervorgehoben. Das Team beschreibt einen Algorithmus, der die komplexen Gleichungen der aktiven Materie in drei Dimensionen und in komplex geformten Geometrien lösen kann. „Unser Algorithmus funktioniert für verschiedene Geometrien in drei Dimensionen und im Zeitverlauf“, sagt Abhinav Singh, einer der Erstautoren der Studie und studierter Mathematiker. Er fährt fort: „Selbst wenn die Datenpunkte nicht gleichmäßig verteilt sind, nutzt unser Algorithmus einen neuartigen numerischen Ansatz, der nahtlos für komplexe biologisch realistische Szenarien funktioniert, um die Gleichungen der Theorie mit hoher Genauigkeit zu lösen. Mithilfe unseres Ansatzes können wir endlich das langfristige Verhalten aktiver Materialien sowohl in bewegten als auch in unbewegten Szenarien verstehen und ihre Dynamik vorhersagen. Darüber hinaus könnten die Theorie und die Simulationen genutzt werden, um biologische Materialien zu programmieren oder molekulare Maschinen auf der Nanoskala zu entwickeln, die nützliche Arbeit leisten.“ Der andere Erstautor, Philipp Suhrcke, Absolvent des Masterstudiengangs Computational Modeling and Simulation der TU Dresden, fügt hinzu: „Dank unserer Arbeit können Wissenschaftlerinnen und Wissenschaftler jetzt zum Beispiel die Form eines Gewebes vorhersagen oder wann ein biologisches Material instabil oder fehlreguliert wird. Das ist bedeutend, um die Mechanismen von Wachstum und Krankheit besser zu verstehen.“
Ein leistungsstarker Code für alle
Das Forschungsteam implementierte den Algorithmus mithilfe der Open-Source-Bibliothek OpenFPM. Damit ist er für Andere frei verfügbar. OpenFPM wurde von der Sbalzarini-Gruppe entwickelt, um wissenschaftliches Rechnen für alle zugänglich zu machen. Die Forscher entwickelten zuerst eine neue Computersprache in OpenFPM , die es ermöglicht, Supercomputer-Codes einfacher und viel schneller zu schreiben. Dadurch muss man nicht jedes Mal bei Null anfangen, wenn man einen Code schreiben möchte, wodurch die Entwicklungszeiten in der wissenschaftlichen Forschung effektiv von Monaten oder Jahren auf Tage oder Wochen verkürzt werden können. Das bringt enormeProduktivitätssteigerungen. Aufgrund des großen Rechenaufwands zur Untersuchung dreidimensionaler aktiver Materialien ist der neue Code dank der Verwendung von OpenFPM auf Multiprozessor-Supercomputern skalierbar. Obwohl der Code für leistungsfähige Supercomputern ausgelegt ist, kann er auch auf normalen Arbeitsplatzrechnern für die Untersuchung zweidimensionaler Materialien genutzt werden.
Der leitende Wissenschaftler der Studie, Ivo Sbalzarini, fasst zusammen: „Zehn Jahre unserer Forschung sind in die Entwicklung dieses Codes geflossen, um die Produktivität computerbasierter Wissenschaft zu verbessern. Dies ist nun alles in einem Werkzeug vereint, um das dreidimensionale Verhalten lebender Materialien zu verstehen. Open-Source, skalierbar und in der Lage, komplexe Szenarien zu bewältigen, eröffnet unser Code neue Möglichkeiten, aktive Materialien zu erforschen. Damit könnten wir endlich verstehen, wie Zellen und Gewebe ihre Form erhalten und damit die grundlegende Frage der Morphogenese beantworten, die Wissenschaftlerinnen und Wissenschaftler seit Jahrhunderten fasziniert. Der Code könnte uns auch dabei helfen, künstliche biologische Maschinen mit minimaler Anzahl von Komponenten zu entwerfen.“
--------
Der Computercode dieser Studie, ist im Github-Verzeichnis 3Dactive-hydrodynamics verfügbar unter: https://github.com/mosaic-group/3Dactive-hydrodynamics
Die Open-Source-Bibiothek OpenFPM ist verfügbar unter: https://github.com/mosaic-group/openfpm_pdata
Veröffentlichungen zur verwendeten Computersprache und der OpenFPM-Softwarebibliothek:
https://doi.org/10.1016/j.cpc.2019.03.007
https://doi.org/10.1140/epje/s10189-021-00121-x
Abhinav Singh*, Philipp H. Suhrcke*, Pietro Incardona, Ivo F. Sbalzarini: A numerical solver for active hydrodynamics in three dimensions and its application to active turbulence. Physics of Fluids 35, 105155 (2023), doi: 10.1063/5.0169546.
*Abhinav Singh and Philipp H. Suhrcke haben zu gleichen Teilen zu dieser Arbeit beigetragen und teilen sich die Erstautorenschaft.
Pressekontakt MPI-CBG:
Katrin Boes
+49 351 210 2080
kboes(at)mpi-cbg.de
Weitere Informationen:
Prof. Dr. Ivo Sbalzarini
+49 (0) 351 210 2525
sbalzarini(at)mpi-cbg.de